聚类算法分层聚类
层次聚类是另一种无监督学习算法,用于将具有相似特征的未标记数据点组合在一起。层次聚类算法分为以下两类:
凝聚层次算法 : 在凝聚层次算法中,每个数据点被视为一个单独的集群,然后依次合并或凝聚(自下而上的方法)集群对。集群的层次结构表示为树状图或树状结构。
分层次算法 : 另一方面,在划分层次算法中,所有数据点都被视为一个大簇,聚类的过程涉及将一个大簇划分(自顶向下方法)为多个小簇。
执行凝聚层次聚类的步骤
我们将解释最常用和最重要的层次聚类,即凝聚。执行相同的步骤如下:
-
步骤 1 : 将每个数据点视为单个集群。因此,我们将在开始时拥有 K 个集群。数据点的数量在开始时也将是 K。
-
步骤 2 : 现在,在这一步中,我们需要通过连接两个 closet 数据点来形成一个大集群。这将导致总共有 K-1 个集群。
-
步骤 3 : 现在,要形成更多的集群,我们需要加入两个壁橱集群。这将导致总共有 K-2 个集群。
-
步骤 4 : 现在,要形成一个大集群,重复以上三个步骤,直到 K 变为 0,即没有更多的数据点可以加入。
-
步骤 5 : 最后制作一个大簇后,会根据问题用树状图分成多个簇。
树状图在凝聚层次聚类中的作用
正如我们在上一步中所讨论的,树状图的作用是在大集群形成后开始的。根据我们的问题,树状图将用于将集群拆分为多个相关数据点集群。可以通过下面的例子来理解:
示例 1
为了理解,让我们从导入所需的库开始,如下所示:
%matplotlib inline import matplotlib.pyplot as plt import numpy as np
接下来,我们将绘制我们为本示例采用的数据点:
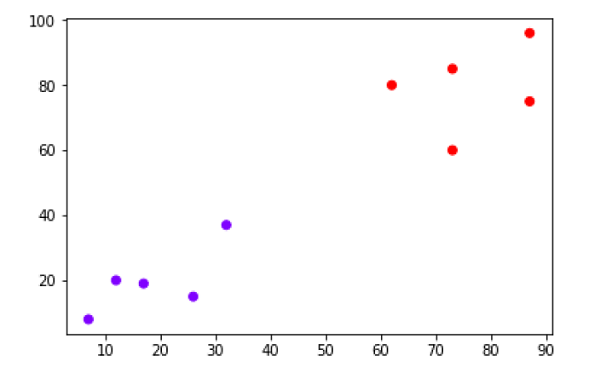
X = np.array([[7,8],[12,20],[17,19],[26,15],[32,37],[87,75],[73,85], [62,80],[73,60],[87,96],]) labels = range(1, 11) plt.figure(figsize=(10, 7)) plt.subplots_adjust(bottom=0.1) plt.scatter(X[:,0],X[:,1], label='True Position') for label, x, y in zip(labels, X[:, 0], X[:, 1]): plt.annotate(label,xy=(x, y), xytext=(-3, 3),textcoords='offset points', ha='right', va='bottom') plt.show()

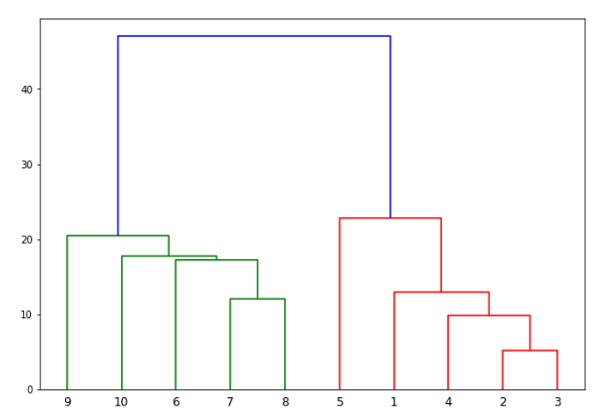
从上图中,很容易看出我们在 out 数据点中有两个集群,但在现实世界的数据中,可能有数千个集群。接下来,我们将使用 Scipy 库绘制数据点的树状图:
from scipy.cluster.hierarchy import dendrogram, linkage from matplotlib import pyplot as plt linked = linkage(X, 'single') labelList = range(1, 11) plt.figure(figsize=(10, 7)) dendrogram(linked, orientation='top',labels=labelList, distance_sort='descending',show_leaf_counts=True) plt.show()
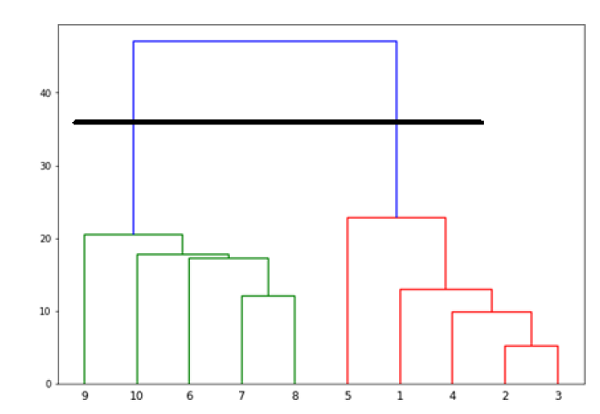
现在,一旦形成大簇,就选择最长的垂直距离。然后通过它绘制一条垂直线,如下图所示。当水平线在两点与蓝线相交时,集群的数量将是两个。
接下来,我们需要导入用于聚类的类并调用其 fit_predict 方法来预测聚类。我们正在导入 sklearn.cluster 库的 AgglomerativeClustering 类:
from sklearn.cluster import AgglomerativeClustering cluster = AgglomerativeClustering(n_clusters=2, affinity='euclidean', linkage='ward') cluster.fit_predict(X)
接下来,借助以下代码绘制集群:
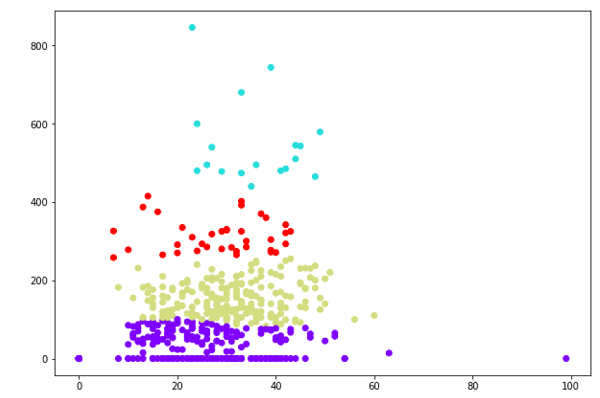
plt.scatter(X[:,0],X[:,1], c=cluster.labels_, cmap='rainbow')
上图显示了我们数据点的两个集群。
例子2
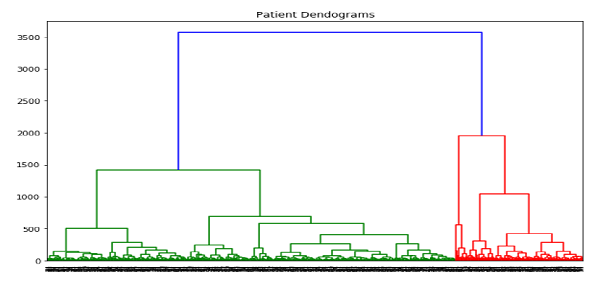
当我们从上面讨论的简单示例中理解了树状图的概念后,让我们转到另一个示例,在该示例中,我们使用层次聚类创建 Pima Indian Diabetes Dataset 中的数据点的聚类:
import matplotlib.pyplot as plt import pandas as pd %matplotlib inline import numpy as np from pandas import read_csv path = r"C:\pima-indians-diabetes.csv" headernames = ['preg', 'plas', 'pres', 'skin', 'test', 'mass', 'pedi', 'age', 'class'] data = read_csv(path, names=headernames) array = data.values X = array[:,0:8] Y = array[:,8] data.shape (768, 9) data.head()
| slno. | preg | Plas | Pres | skin | test | mass | pedi | age | class |
|---|---|---|---|---|---|---|---|---|---|
| 0 | 6 | 148 | 72 | 35 | 0 | 33.6 | 0.627 | 50 | 1 |
| 1 | 1 | 85 | 66 | 29 | 0 | 26.6 | 0.351 | 31 | 0 |
| 2 | 8 | 183 | 64 | 0 | 0 | 23.3 | 0.672 | 32 | 1 |
| 3 | 1 | 89 | 66 | 23 | 94 | 28.1 | 0.167 | 21 | 0 |
| 4 | 0 | 137 | 40 | 35 | 168 | 43.1 | 2.288 | 33 | 1 |
patient_data = data.iloc[:, 3:5].values
import scipy.cluster.hierarchy as shc
plt.figure(figsize=(10, 7))
plt.title("Patient Dendograms")
dend = shc.dendrogram(shc.linkage(data, method='ward'))
from sklearn.cluster import AgglomerativeClustering cluster = AgglomerativeClustering(n_clusters=4, affinity='euclidean', linkage='ward') cluster.fit_predict(patient_data) plt.figure(figsize=(10, 7)) plt.scatter(patient_data[:,0], patient_data[:,1], c=cluster.labels_, cmap='rainbow')