Biopython 绘图
本章介绍如何绘制序列。在转到这个主题之前,让我们了解绘图的基础知识。
Plotting
Matplotlib 是一个 Python 绘图库,可生成各种格式的高质量图形。我们可以创建不同类型的图表,如折线图、直方图、条形图、饼图、散点图等。
pyLab 是属于 matplotlib 的一个模块,它结合了数值模块 numpy 和图形绘图模块 pyplot。 Biopython 使用 pylab 模块来绘制序列。为此,我们需要导入以下代码:
import pylab
在导入之前,我们需要使用 pip 命令安装 matplotlib 包,命令如下:
pip install matplotlib
示例输入文件
创建一个名为的示例文件 绘图.fasta 在你的 Biopython 目录中并添加以下更改:
>seq0 FQTWEEFSRAAEKLYLADPMKVRVVLKYRHVDGNLCIKVTDDLVCLVYRTDQAQDVKKIEKF >seq1 KYRTWEEFTRAAEKLYQADPMKVRVVLKYRHCDGNLCIKVTDDVVCLLYRTDQAQDVKKIEKFHSQLMRLME >seq2 EEYQTWEEFARAAEKLYLTDPMKVRVVLKYRHCDGNLCMKVTDDAVCLQYKTDQAQDVKKVEKLHGK >seq3 MYQVWEEFSRAVEKLYLTDPMKVRVVLKYRHCDGNLCIKVTDNSVCLQYKTDQAQDV >seq4 EEFSRAVEKLYLTDPMKVRVVLKYRHCDGNLCIKVTDNSVVSYEMRLFGVQKDNFALEHSLL >seq5 SWEEFAKAAEVLYLEDPMKCRMCTKYRHVDHKLVVKLTDNHTVLKYVTDMAQDVKKIEKLTTLLMR >seq6 FTNWEEFAKAAERLHSANPEKCRFVTKYNHTKGELVLKLTDDVVCLQYSTNQLQDVKKLEKLSSTLLRSI >seq7 SWEEFVERSVQLFRGDPNATRYVMKYRHCEGKLVLKVTDDRECLKFKTDQAQDAKKMEKLNNIFF >seq8 SWDEFVDRSVQLFRADPESTRYVMKYRHCDGKLVLKVTDNKECLKFKTDQAQEAKKMEKLNNIFFTLM >seq9 KNWEDFEIAAENMYMANPQNCRYTMKYVHSKGHILLKMSDNVKCVQYRAENMPDLKK >seq10 FDSWDEFVSKSVELFRNHPDTTRYVVKYRHCEGKLVLKVTDNHECLKFKTDQAQDAKKMEK
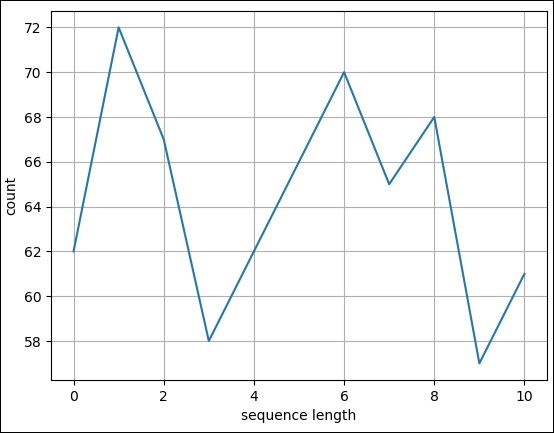
线图
现在,让我们为上述 fasta 文件创建一个简单的线图。
步骤 1 : 导入SeqIO模块读取fasta文件。
>>> from Bio import SeqIO
步骤 2 :解析输入文件。
>>> records = [len(rec) for rec in SeqIO.parse("plot.fasta", "fasta")]
>>> len(records)
11
>>> max(records)
72
>>> min(records)
57
步骤 3 : 让我们导入pylab模块。
>>> import pylab
步骤 4 : 通过分配 x 和 y 轴标签来配置折线图。
>>> pylab.xlabel("sequence length")
Text(0.5, 0, 'sequence length')
>>> pylab.ylabel("count")
Text(0, 0.5, 'count')
>>>
步骤 5 : 通过设置网格显示来配置折线图。
>>> pylab.grid()
步骤 6 : 通过调用 plot 方法并提供记录作为输入来绘制简单的折线图。
>>> pylab.plot(records) [<matplotlib.lines.Line2D object at 0x10b6869d 0>]
步骤 7 : 最后使用下面的命令保存图表。
>>> pylab.savefig("lines.png")
Result
执行上述命令后,你可以在 Biopython 目录中看到以下图像。
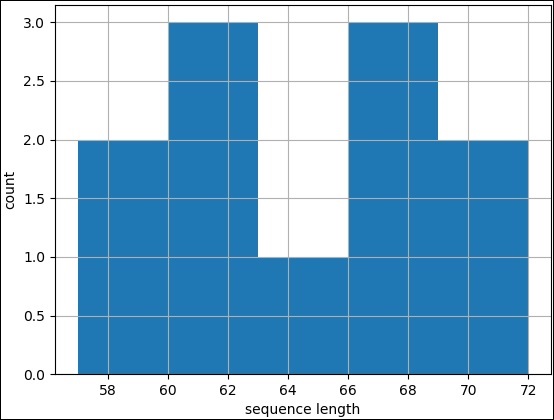
直方图
直方图用于连续数据,其中 bin 表示数据范围。除了 pylab.plot 之外,绘制直方图与折线图相同。相反,调用 pylab 模块的 hist 方法,其中包含记录和 bin 的一些 custum 值(5)。完整的编码如下:
步骤 1 : 导入SeqIO模块读取fasta文件。
>>> from Bio import SeqIO
步骤 2 :解析输入文件。
>>> records = [len(rec) for rec in SeqIO.parse("plot.fasta", "fasta")]
>>> len(records)
11
>>> max(records)
72
>>> min(records)
57
步骤 3 : 让我们导入pylab模块。
>>> import pylab
步骤 4 : 通过分配 x 和 y 轴标签来配置折线图。
>>> pylab.xlabel("sequence length")
Text(0.5, 0, 'sequence length')
>>> pylab.ylabel("count")
Text(0, 0.5, 'count')
>>>
步骤 5 : 通过设置网格显示来配置折线图。
>>> pylab.grid()
步骤 6 : 通过调用 plot 方法并提供记录作为输入来绘制简单的折线图。
>>> pylab.hist(records,bins=5) (array([2., 3., 1., 3., 2.]), array([57., 60., 63., 66., 69., 72.]), <a list of 5 Patch objects>) >>>
步骤 7 : 最后使用下面的命令保存图表。
>>> pylab.savefig("hist.png")
Result
执行上述命令后,你可以在 Biopython 目录中看到以下图像。
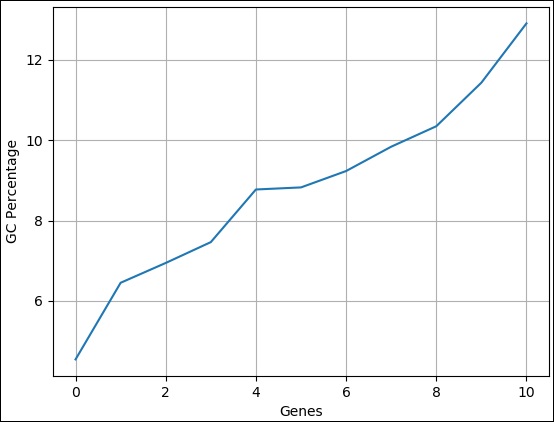
GC 序列百分比
GC百分比是比较不同序列的常用分析数据之一。我们可以使用一组序列的 GC 百分比做一个简单的折线图并立即进行比较。在这里,我们可以将数据从序列长度更改为 GC 百分比。完整的代码如下:
步骤 1 : 导入SeqIO模块读取fasta文件。
>>> from Bio import SeqIO
步骤 2 :解析输入文件。
>>> from Bio.SeqUtils import GC
>>> gc = sorted(GC(rec.seq) for rec in SeqIO.parse("plot.fasta", "fasta"))
步骤 3 : 让我们导入pylab模块。
>>> import pylab
步骤 4 : 通过分配 x 和 y 轴标签来配置折线图。
>>> pylab.xlabel("Genes")
Text(0.5, 0, 'Genes')
>>> pylab.ylabel("GC Percentage")
Text(0, 0.5, 'GC Percentage')
>>>
步骤 5 : 通过设置网格显示来配置折线图。
>>> pylab.grid()
步骤 6 : 通过调用 plot 方法并提供记录作为输入来绘制简单的折线图。
>>> pylab.plot(gc) [<matplotlib.lines.Line2D object at 0x10b6869d 0>]
步骤 7 : 最后使用下面的命令保存图表。
>>> pylab.savefig("gc.png")
Result
执行上述命令后,你可以在 Biopython 目录中看到以下图像。